【讲座笔记】阿斯利康计算机辅助药物设计讲座
利用人工智能加速药物研发——小分子及其他领域 - 总结提纲
前言: 本次在线讲座由BioSolveIT公司主办,邀请了瑞典阿斯利康的Eva Nittinger博士主讲。讲座主题为"利用人工智能加速药物研发——小分子及其他领域"。本文是笔者整理的讲座笔记,供中文研究者参考。
1. 药物发现过程概述
1.1 DMTA循环的核心地位
- DMTA循环:设计(Design) → 制备(Make) → 测试(Test) → 分析(Analyze)
- 时间挑战:从化学起始点(hit)到候选药物(CD)需要3年以上
- 加速目标:如何通过计算方法加速这一过程
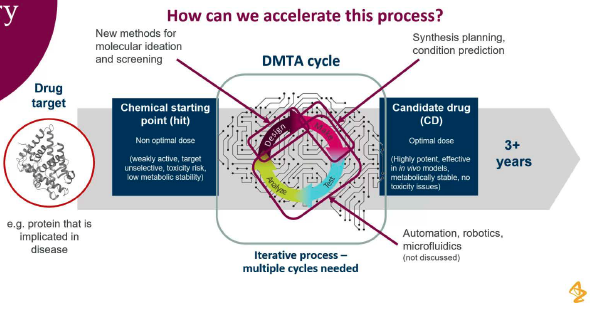
1.2 计算机辅助药物设计的复杂性
- 硅内靶点评估:3D结构预测、结合模式、模式选择
- 化学空间探索:命中识别、化学系列选择、知识产权分析
- 化合物谱优化:多参数(>100)优化、平衡相互关联和对立因素
2. 蛋白质折叠与结构预测
2.1 AlphaFold的成功应用案例
- 分子替换模板:X射线晶体学中的应用
- 功能预测:通过预测数据补充实验数据
- 结构动力学:探索AlphaFold是否能预测蛋白质动态变化
2.2 结构预测方法的局限性
优势领域:
- 单一结构解析
- 强蛋白质-蛋白质相互作用
不适用领域:
- 动态和结构运动
- 新型模式(如PROTACs)
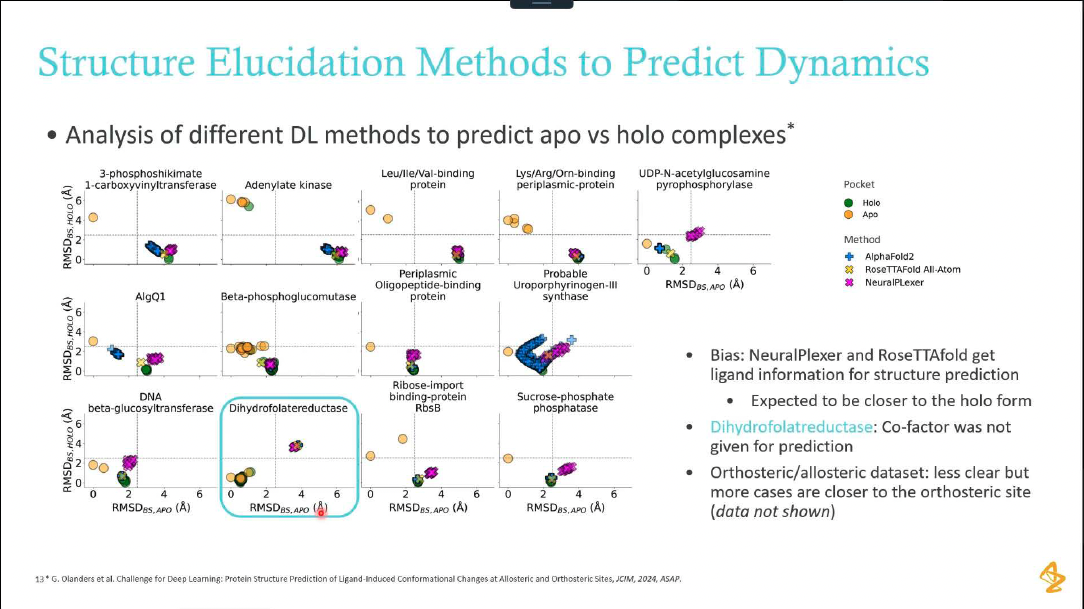
2.3 深度学习方法比较
- 多种方法评估:AlphaFold2、RoseTTAFold、NeuralPlexer等
- 结合状态预测:开放态(apo)vs闭合态(holo)结构预测
- 偏差分析:NeuralPlexer和RoseTTAFold在配体信息获取方面的优势
3. 化学空间探索与利用
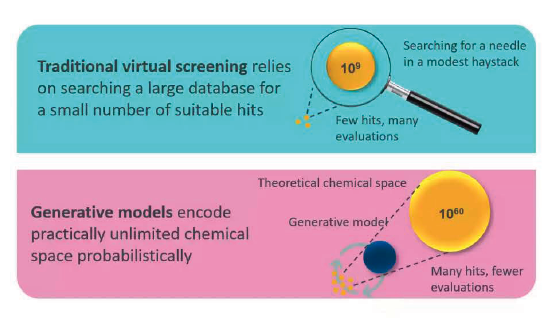
3.1 生成式建模 vs 虚拟筛选
传统虚拟筛选:
- 在大型数据库中搜索,寻找少量合适的命中化合物
- 类似"大海捞针"的过程
生成式模型:
- 以概率方式编码几乎无限的化学空间
- 更高效的化学空间探索